1.2试验方法
1.2.1突变株及回补菌株的获得参考青枯雷尔氏菌GMI1000hrcN基因设计引物hrcN-F(5′-GGCTGAT ATCGGATCCATGACCCATCTCGCGCTG-3′)和hrcN-R(5′-GGTGGTGGTGCTCGATCATGCCAGTGCG ATCTCGTC-3′)。提取CBM613菌株DNA,PCR扩增。将回收的DNA片段连接到T载体,转化DH5α大肠杆菌,挑取PCR验证过的阳性克隆菌株测序。利用Krogh等的方法预测分子量、PI、跨膜区域和亲水性;利用深度神经网络SignalP 5.0预测信号肽;利用clustalw在线比对hrcN的基因和蛋白质序列;Motif预测蛋白功能采用Nicolas等的方法;在线预测蛋白亚细胞定位。
根据hrcN基因及上下游序列、庆大霉素(Gm)抗性基因序列设计引物(表1),首先扩增出hrcN基因上、下游同源重组臂序列,从pJQ200SK质粒上扩增Gm抗性基因编码序列;然后利用融合PCR技术构建打靶序列片段(hrcN基因上游-Gm-hrcN基因下游),经SmaI酶切完成打靶载体pCVD442-ΔhrcN::Gm的构建;最后通过同源重组和电转化大肠杆菌,与受菌体(CBM613菌株)结合,在含Gm的NB培养基上筛选突变株,并用表1中的鉴定引物鉴定突变株。

表1 hrcN基因敲除所需引物
通过hrcN-1F/hrcN-1R扩增出hrcN片段,经XbaI/EcoR I酶切后克隆入pRK415质粒对应的酶切位点,经连接和转化TOP10化学感受态细胞后,铺四环素(Tc)平板筛选阳性克隆,完成pRK415-hrcN基因回补质粒构建。回补质粒pRK415-hrcN电转化大肠杆菌,与受体菌(CBM613/ΔhrcN)结合,在含Tc的TSB培养基上筛选回补菌株,用pRK415-F/pRK415-R引物进行PCR鉴定回补菌株。
1.2.2表型测定
番茄感病品种为中蔬5号,按照He等根部接种法接种菌株CBM613、CBM613/ΔhrcN突变株和CBM613/ΔhrcN-p-hrcN回补菌株各接种15株,3次重复。按照Meng等的方法计算青枯病的病情指数;分别挑取3种菌株于NB培养基中,28℃、220 r/min摇床培养获得菌悬液,10000 r/min离心5 min收集菌体。按照Kanda等方法测定600 nm的吸光度值,计算生长曲线;取浓度为3×108CFU/mL的野生型菌株、突变株和回补菌株菌液各5μL,3种菌株的泳动性检测按照Kelman等方法测量菌落直径。3种菌株的生物被膜的测定参考Meng等的方法测定490 nm的吸光度值。
2结果与分析
2.1 hrcN基因的扩增结果
PCR产物在1%琼脂糖凝胶进行电泳,图1结果显示,条带清晰而且特异,大小1300 bp左右。将该条带回收,然后连接到T载体并且转化大肠杆菌,得到的阳性克隆进行菌落PCR鉴定并测序,测序发现基因长度为1320 bp,共编码439个氨基酸,结果表明已扩增出番茄青枯雷尔氏菌CBM613的hrcN基因,DNA序列已提交到GenBank(Gene ID:No.42594317)。预测HrcN蛋白分子量为47.54 kD,PI为4.97,无信号肽(预测有信号肽概率为1.734%),无跨膜区域,整体呈弱亲水性(图2)。Motif预测结果显示该蛋白为ATP酶,蛋白亚细胞定位预测其定位于细胞内膜和细胞质。
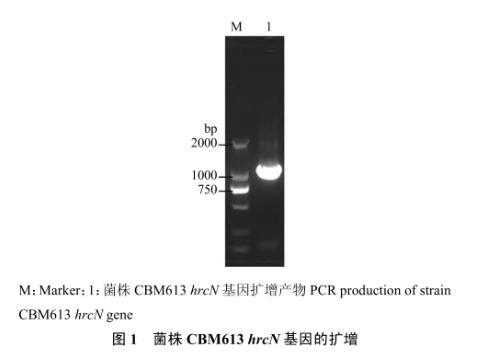
图1菌株CBM613 hrcN基因的扩增
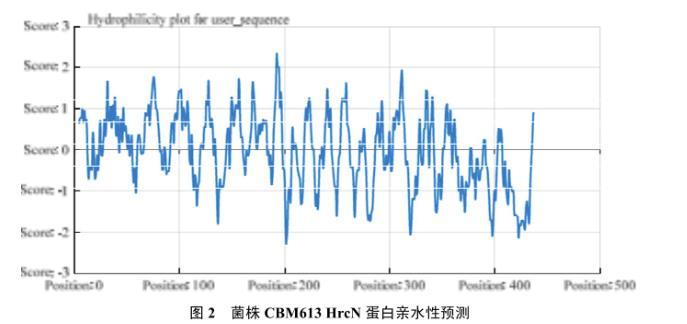
图2菌株CBM613 HrcN蛋白亲水性预测
通过与菌株GMI1000的hrcN基因序列进行在线比对发现,该基因一致性为99.6%,在青枯雷尔氏菌中非常保守。青枯雷尔氏菌与参比菌株GMI1000hrcN基因相比共有5个SNP位点,具体突变信息为216:A-G GTA-GTG val;609:T-C CGT-CGC arg;879:T-C CGT-CGC arg;907:G-A GCC-ACC ala-thr;999:T-C GGT-GGC gly。只有907位氨基酸发生改变(由GMI1000的丙氨酸突变为苏氨酸),其他5个SNP都是无意突变。
相关新闻推荐
3、噬菌体ΦSboM-AG3的一步生长曲线及29个志贺氏菌菌株上AG3的宿主范围
